続・4.5SHは蜜の味(6)最終章
研究というのはとかく思い通りにいかず、交差点ごと赤信号がデフォルトでしょ、と思っていましたが、仕事によってはcriticalなポイントを超えたらあとは揃ったパズルのピースをバチバチはめるだけ、そういうこともありうるのだということをこの歳になって知ることができたのは、まさに僥倖の極みでした。
まずびっくりしたのがレポーター遺伝子の実験です。選択的スプライシングの研究ではアデノウイルスのイントロンに標的のエクソンと前後のイントロン配列をいれたレポーター遺伝子を作ることが多いらしいのですが、4.5SHが100%スキッピングさせている標的異常エクソンを入れたレポーターを4.5SHを持たないヒトの細胞に導入すると、なんの疑いもなくエクソンとして認識されて、完璧にスプライシングされるというデータを芳本くんが出してきました。もうちょっときちんと見なくていいんですか、ヒト細胞さん、とこちらが心配になるぐらい。そこに4.5SHの発現ベクターを同時に導入すると、100%ではないですが、きれいにスキッピングが誘導されます。
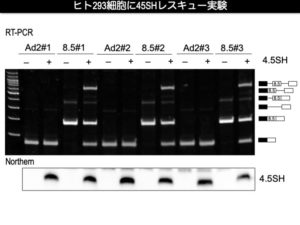
芳本くんが送ってくれた最初のレポーター実験のデータ。293細胞ではエクソン8.5(Slc25a40のintron8に現れるエクソン)は完璧にスプライシングされているのが、4.5SHの過剰発現でスキップされるようになる。Ad2は元のレポータ遺伝子。
実験って、こんなうまくいくもんなんだ。過剰発現でもKOでもうんともすんとも言わないのがデフォルトのlncRNA研究業界で長らく過ごしてきたので、ncRNAの分子機能をこれだけクリアーにread outできる実験系ができるというのは、個人的にはこれはもう特ダネのレベルです。
さらに芳本さんのクリーンヒットは続きます。僕はそれまで4.5SHはアンチセンス核酸とおなじようにベタッとエクソンに張り付いて物理的にスプライシングを阻害しているものとばかり思っていたのですが、芳本さんいわく、4.5SHの5’側にあるステムループ構造は、標的エクソンと塩基対を作らないことが多いとのこと。これ、ぜったいなんかのエフェクターに結合してますよ、と力説するのですが、いやいやいやそれはないでしょ、ちょっと妄想入ってない、と僕自身は思っていました。ところが、早速芳本くんが4.5SHのステムループ構造を配列が良く似たSINE B1のステムループ構造に変えた分子を作ってアッセイすると、標的配列との相補性はむしろ増すのに、エクソンスキッピング活性は劇的に低下するではありませんか。
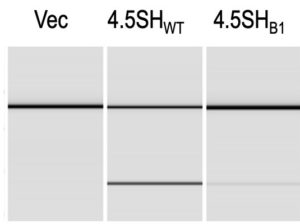
4.5SHに特徴的な5’側のステムループ部分を5塩基だけ違うSINE B1のステムループに変えると活性がほぼ喪失。ステムループだいじということが証明された瞬間。
僕の説はあっさり敗北。データは偉大、真実は強し、です。ダメ押しだったのが、4.5SHのステムループ配列を全く別のエクソンのアンチセンス配列と結合したキメラ分子を作ると、そのエクソンのスキッピングが誘導されるという驚きの芳本くんのデーター。任意のエクソンをスキッピングさせることのできる人工キメラRNAまで出来ちゃいました。

芳本くんが作った任意のエクソンのスキッピングを誘導するキメラRNA。特許もこれで取れました。
さて、そうなると、4.5SHのステムループは標的と結合するのではなく、なんらかのエフェクター分子と結合していることになります。少しは僕も手を動かさないと、ということで、4.5SHのステムループRNAを合成して、適当にリンカーつけてビオチンつけて、念の為に5’にリン酸もつけて、Neuro2Aの核をsonicationしたlysateを使って、pull down。良く似たSINE B1のステムループでは活性がないことが分かっていたので、それをコントロールに用いました。すると、washの段階から、ビーズの様子がコントロールと4.5SHでは明らかに違います。これ、絶対なんかある、絶対できてる、と念じながら銀染色の現像液をゆらゆらしてたら
おおーっ!きたきたきたきた!
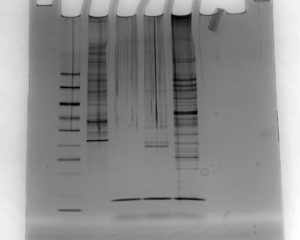
左からマーカー、input (10%)、ビーズのみ、SL1 SINE B1、SL1 4.5SHのpull down。泳動槽きちんと洗ってなくて縦の筋がいっぱい入ってますが、結果は火を見るより明らか。
RNAを用いたpull down実験はこれまでも何回か試したことはあって、だいたいが見た目ほとんど一緒だけれどもわずかに見られる特異的なバンドを追いかけることばかりだったのですが、めちゃめちゃキレイに差が出ています。条件をきつくして洗ってみたらどうですかという芳本さんのアドバイスにしたがって洗ってみると、きれいに一本だけバンドが残ることもわかりました。学術変革の質量分析担当の尾山さんのところで早速同定してもらったところ、このバンドの正体はhnRNP M。4.5SHはhnRNP Mにガッツリくっついて、それがSfpqやNonoなどのイントロン結合タイプのRNA結合タンパク質をごっそり引き連れてくるということがわかりました。ノックダウン実験とtethering実験も、材料はすべて廣瀬さんと山崎さんがお持ちだったこともあり、ごそっと材料をもらってこれまた芳本さんが超速で実験を進めた結果、すべて予想通り。運命の9/7からここまで半年たらず。ワイルドスピード森川葵さんも真っ青の快進撃です。
でも、、、
楽しかったのはここまでで、あの雑誌やらあの雑誌やらあの雑誌に投稿したら全てeditorial reject。判で押したように、「アンチセンス核酸医薬ってあるでしょ?核酸がエクソンをスキッピングさせるというのはconceptually not entirely newでないから私達のjournalはちょっとダメね。でも、姉妹誌のオープンアクセスのジャーナルでこんなんあるの。あなたの論文に、すごく気があるみたいよ。じゃね。」という回答でした。はあぁ?全く何を言っているのかわからない、誰がアンチセンス核酸の話しした?これ、endogenousの遺伝子ですよ?しかも、オンオフで選択的スプライシングを制御する初めてのncRNAですよ?しかもなぜ4.5SHはSINE B1を持つ種でしかないかという進化の謎までとけちゃったかもしれないんですよ?とだいぶ反論はしたのですが、ただいたずらに放置プレーを食らうだけで、結局思わしい戦果は得られませんでした。一度はレフリーに回っておおかた好意的なコメントだったのですが、editorの最初のdecisionは覆らず。悔しいを通り越して呆れ返る、といった心持ちでした。
一方、この仕事を初めてお披露目したのはCold Spring Harbor Laboratory MeetingのNoncoding Genomeだったのですが、peerな人たちは口々に面白いと言ってくれて、それはたいそう励みになりました。特に、short noncoding RNA研究の生き字引、4.5SHを原田文夫さんが同定されたころから良く経緯を知っておられるSandra Wollinさんが、めちゃくちゃ面白いじゃない!と声をかけてくださったのは、やたーっ!、という感じでとても嬉しく、論文で苦労している間もずっと応援してくださって、その励ましの言葉のお陰で論文の出版までこぎつけることが出来たと言っても過言ではありません。負け惜しみっぽくなりますが、editorに認められなくっても、面白いと言ってもらいたい人に面白いと言ってもらえたほうが、気分的には高揚するものがありますし、論文は所詮論文なので、今回の発見がこれからどれだけ学問的な価値を生み出すのか、そこで研究の真価が問われるのでしょう。
ともあれ、自分史上最高に面白い研究に関わることが出来て、いままで生きてきて一番幸せでした(ぜんぜんかわいくない)。それにしても、と思うのは、この研究、あとから振り返ってみたらあれが伏線だったのかということの連続でした。大塚さんとの出会い、トクロンさんとの出会い、CARDの人々との出会い、荒木さんとの出会い、そしてパンチの効いた芳本さんとの出会い。予想ができないからこそ研究は面白いし、先が見えないからこそ、研究はかけがえがないものなのでしょう。そして、4.5SHの発見者である原田文夫さんと原田さんと共に4.5SHの配列を決めた加藤宣之さんは、共に北大薬学部のOB。これって、ただの偶然なのでしょうか。
昨日、今日。明日、明後日。そのときは気づかなくても、10年後、20年後、また将来回収することになる新たな伏線になるような出来事が、これからもずっと続いていくのだと思います。いろいろな人が紡いできた糸が交わるところで次の研究が生まれる。そうやって糸を紡ぎ続けていくことが、研究者の、生業なのかもしれません。素晴らしきかな、研究人生。
(了)
投稿者プロフィール

最新の投稿
 ノンドメインブログ2025.06.27来し方行末~パート1
ノンドメインブログ2025.06.27来し方行末~パート1 ノンドメインブログ2025.02.11平和な日々
ノンドメインブログ2025.02.11平和な日々 ノンドメインブログ2024.11.25MBSJ2024のシンポジウムのすごいゲスト
ノンドメインブログ2024.11.25MBSJ2024のシンポジウムのすごいゲスト ノンドメインブログ2024.09.17奇遇癖
ノンドメインブログ2024.09.17奇遇癖


